-
Jess Tate
Rob MacLeod
SCI Seg3D Mailing List
Text archives Help
- From: Ayla Khan <ayla@sci.utah.edu>
- To: Andrew Effat <andrew.effat@mail.utoronto.ca>
- Cc: Elizabeth Jurrus <liz@sci.utah.edu>, "seg3d@sci.utah.edu" <seg3d@sci.utah.edu>
- Subject: [Seg3D] Re: SEG3D2 interpolating
- Date: Wed, 7 Aug 2013 23:35:12 -0600
Hi Andrew,
That error message is generated by the Tetgen meshing tool when the longest
possible edge length formed by the set of input points is zero, in this case
the points in the junctions/particle-union.node file. Have a look the file
and see if there was a problem writing it out in the previous stage. Also,
junctions/particle-union.node is based on junctions/particle-union.pts, which
you can visualize in SCIRun (import as a point cloud using the ReadField
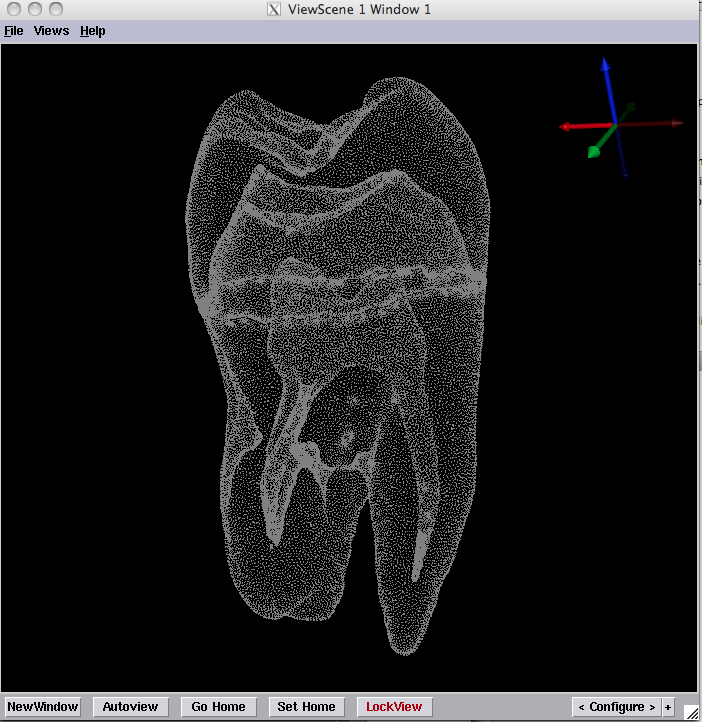
module). I've attached an example of what the tutorial example looks like at
this stage (also Figure 5.4 in the BioMesh tutorial). If the point cloud
doesn't follow the expected shape of your segmentation, have a look at the
output and files from the previous stages to see if there are any warning
messages etc.
Ayla
On Aug 7, 2013, at 12:03 AM, Andrew Effat wrote:
> Hey Ayla,
>
> I'm having trouble going through the process with my own data. I believe
> the issue is with stage 6, running particle system. The output folder is
> missing a number of the files that should have been created after it has
> been executed. It still finishes up, but then stage 7 does not process.
> This is the error I receive when I try to run stage 7:
>
> Stage 7 -- Generate Surface Mesh
> ***************
> "/usr/bin/python" -u
> "/Users/andrew/Desktop/Summer-2013-Research/SCIRun/SCIRun.app/Contents/Resources/bin/FEMesher/BuildMaterialInterfaceMesh.py"
> "/Users/andrew/Desktop/Summer-2013-Research/biomeshfiles/model_config.txt"
> "/Users/andrew/Desktop/Summer-2013-Research/SCIRun/SCIRun.app/Contents/Resources/bin"
> "/Users/andrew/Desktop/Summer-2013-Research/SCIRun/SCIRun.app/Contents/Resources/bin/pts2node"
> junctions/particle-union.pts junctions/particle-union.node
> "/Users/andrew/Desktop/Summer-2013-Research/SCIRun/SCIRun.app/Contents/Resources/bin/tetgen"
> junctions/particle-union.node
> Opening junctions/particle-union.node.
> Error: The point set is trivial.
> Program stopped.
>
> I'm not certain what the issue is.
>
> Please let me know which part you'd like me to provide more detailed
> information on,
>
> Thanks,
>
> Andrew
> From: Ayla Khan [ayla@sci.utah.edu]
> Sent: Wednesday, August 07, 2013 1:43 AM
> To: Andrew Effat
> Cc: Elizabeth Jurrus; seg3d@sci.utah.edu
> Subject: Re: SEG3D2 interpolating
>
> Hi Andrew,
>
> Chapter 6 of the BioMesh3D tutorial (pdf) explains how to go from
> segmenting your data in Seg3D to isolate the structures that you want to
> mesh, to creating a volume mesh in BioMesh3D. The data used in the tutorial
> example is from the SCIRunData download.
>
> Please let me know if there is anything in the tutorial that is unclear.
>
> Ayla
>
> On Aug 6, 2013, at 2:51 PM, Andrew Effat wrote:
>
>> Hey,
>>
>> I'm not certain to be honest. I am importing a set of Cad images into
>> SEG3D as a volume. I am then exporting them from SEG3D as an nrrd file and
>> I would like to use the biomesh program to create a mesh out of that file.
>> I am wondering if the seg3d program has the ability to interpolate between
>> the images and create a smooth and continuous 3D volume. As I scroll
>> through the planes in seg3d it just rolls between each image separately.
>>
>> Thank you,
>>
>> Andrew
>> From: Elizabeth Jurrus [liz@sci.utah.edu]
>> Sent: Tuesday, August 06, 2013 4:39 PM
>> To: Andrew Effat
>> Cc: Ayla Khan
>> Subject: Re: SEG3D2 interpolating
>>
>> Hi Andrew,
>>
>> Can you be more specific? Are your nrrd files binary and you just need to
>> mesh the volume?
>>
>> I've cc'd Ayla (our lead seg3d developer) to help with your questions.
>>
>> - liz
>>
>>
>> On 8/6/13 1:34 PM, Andrew Effat wrote:
>>> Hello Liz,
>>>
>>> I was wondering if you could tell me if the SEG3D2 program had the
>>> ability to interpolate between a set of images to create a 3D structure.
>>> I am importing a data set of JPEG files and importing them as NRRD files
>>> to be able to use them with the Biomesh3d program.
>>>
>>> Thank you,
>>>
>>> Andrew
- [Seg3D] Re: SEG3D2 interpolating, Ayla Khan, 08/06/2013
- Message not available
- [Seg3D] Re: SEG3D2 interpolating, Ayla Khan, 08/07/2013
- Message not available
Archive powered by MHonArc 2.6.16.